AHCY i poziom homocysteiny.
styczeń 4, 2018 by Jarek
Kategoria: MTHFR i inne polimorfizmy
“Jeżeli mam wysoką homocysteinę a nie mam polimorfizmu MTHFR, MTRR to czego powinnam szukać?” Wkraczamy na kolejny pułap wiedzy wydaje mi się. Znamy już kluczowe geny dla cyklu kwasu foliowego, cyklu kobalaminy, więc szukamy dalej!
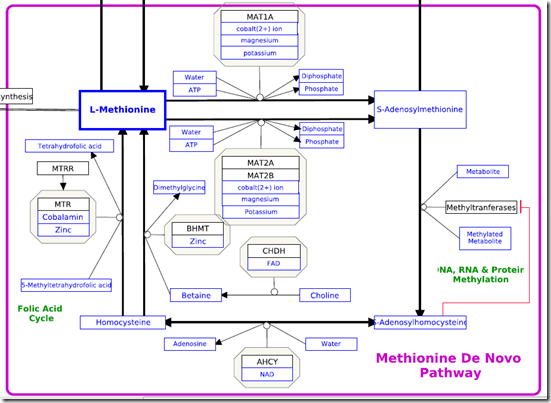
Jaką rolę pełni gen AHCY? Jest genem odpowiedzialnym za degradację adenozylohomocysteiny na adenozynę i homocysteinę. Co oznacza, że homocysteina, która jest dostarczana do organizmu w diecie, potem jest remetylowana do postaci metioniny (dodana jest grupa metylowa) i służy jako podstawowy donor grup metylowych w postaci S-adenozylometioniny (SAMe), jest dzięki genowi AHCY znów homocysteiną. Oznacza to, że homocysteina jest stale obecna w organizmie i jej ilość jest też związana z funkcjonowaniem tego genu. jeżeli on będzie źle działał w organizmie będzie więcej metioniny, gdy będzie działał za szybko, będzie zbyt dużo homocysteiny. Jak to wygląda na wykresach, popatrzcie poniżej.
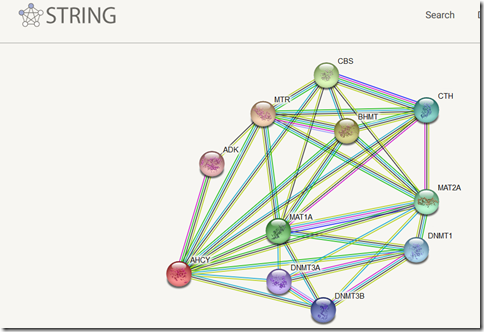
Po pierwsze spójrzmy na String. Ścieżka wzajemnych relacji z genem MAT1, BHMT, CBS, MTR jest oczywista i wynika z ze ścieżki metylacji. Geny te oddziaływują na siebie co jest oczywiste. Ściśle na efektywność tego genu oddziaływuje cała rodzina genów DNMT3 i vice versa. W ZD przypomnę mamy potrojony gen DNMT3L, który ściśle jest zależny od aktywności i działania genów DNMT3A i DNMT3B.
https://pl.wikipedia.org/wiki/Metylotransferazy_DNA
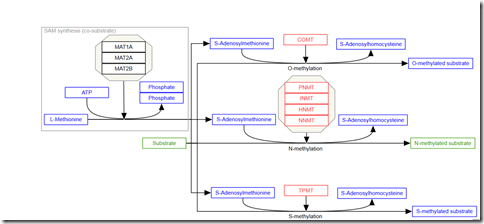
Innym czynnikiem wpływającym na efektywność pracy genu AHCY są metylotransferazy jak PNMT, HNMT, ASMT, GNMT, INMT i COMT (przykłady).
https://www.wikipathways.org/index.php/Pathway:WP704
Jakie polimorfizmy są tutaj zagrożeniem?
Według Amy Yasko musimy zwrócić uwagę na następujące polimorfizmy:
- rs819147 – AHCY-01 (Risk Allele: C)
- rs819134 – AHCY-02 (Risk Allele: G)
- rs819171 – AHCY-19 (Risk Allele: C)
Analizowane polimorfizmy są typologią spowolniającą proces i tworzącą blokadę konwersji adenozylohomocysteiny, przez co występuje zwiększona ilość metioniny, określana jako hypermetioniną. W efekcie cała metylacja jest wyhamowana i tworzą się nadmiary adenozylohomocysteiny, metylotransferazy nie otrzymują swoich grup metylowych negatywnie wpływając na replikację DNA, RNA, metylację białek i tłuszczy.
https://www.nature.com/articles/5201237.pdf?origin=ppub
https://pdfs.semanticscholar.org/0a35/9a320ddd8f108a7243cde009cb8566948c46.pdf
https://www.sciencedirect.com/science/article/pii/S0925443912002165
Zgodnie z badaniami wysoki poziom homocysteiny jest związany ze wzrostem adenozylohomocysteiny powodując hypometylację. Także wskazuje się na wysoki poziom homocysteiny tytułem inhibicji jej remetylacji poprzez nadmierne ilości adenozylohomocysteiny.
W panelach gen ten nie jest powszechnie badany.
Postępowanie w przypadku wystąpienia tego polimorfizmu to:
-dieta nisko metioninowa
-suplementacja NAD+, witaminą NR
-inhibicja cyklu metioniny poprzez suplementację fosfatydylocholiną, kreatyniną i cysteiną
Polimorfizmy AHCY mają istotne znaczenie dal całej metylacji. Popatrzmy na te przypadki:
*osoba z polimorfizmem MTHFR C677T powodująca istotne braki kwasu foliowego na poziomie nawet wyższym niż 30%, przy polimorfizmie AHCY nie prezentuje typowych dla tego typu deficytów wysokich poziomów homocysteiny. W badaniach osoby takie mają zazwyczaj między 9 a 15 umol/l
*osoba z polimorfizmem MTHFR C677T, BHMT, ale i CBS może mieć zupełnie inny poziom homocysteiny, niż wynikałoby to z polimorfizmów, gdyż na poziomie ok.7-8 umol/l
*osoba z polimorfizmem AHCY, może “ukrywać” polimorfizmy CBS, gdyż poziom tauryny w takim przypadku będzie normalny
Typowe objawy polimorfizmów AHCY to brak odpowiedniej detoksykacji, przez to pojawiają się problemy jelitowe i trawienne.
Badania jakie warto w tym zakresie zrobić to oczywiście poziom amoniaku i fumaranu.
https://pl.wikipedia.org/wiki/Kwas_fumarowy
Przyjmuje się także konieczność zrobienia badań w kierunku ilościowego poziomu SAH (adenozylohomocysteiny) i porównania jej do poziomu SAM (adenozylometioniny).
Nie ulega wątpliwości, że badania homocysteiny, kwasu foliowego, holoTC, witaminy D3 są tutaj wspomagające.